Réparation de l'ADN : ATM s’oppose aux liaisons dangereuses
Plusieurs mécanismes de réparation des cassures de l’ADN ont été caractérisés. Mais la manière dont s’effectue le choix entre ces mécanismes est moins connue. Une publication parue dans la revue Nucleic Acids Research révèle comment la voie de réparation adéquate est sélectionnée en présence de cassures de l’ADN particulières, à la base de la toxicité de certaines molécules anticancéreuses. Perturber le choix entre les voies de réparation pourrait offrir une perspective pour améliorer l’efficacité de ces traitements.
Pour éradiquer les cellules cancéreuses, la plupart des traitements non chirurgicaux utilisent des agents physiques (rayonnements) ou des molécules chimiothérapeutiques qui endommagent l’ADN. Le dommage le plus toxique pour une cellule est la cassure de la double chaîne d’ADN de son génome (appelée Cassure Double-Brin ou CDB), qui selon son l’agent causal peut présenter une seule ou deux extrémités. Les CDB à deux extrémités sont réparées très efficacement par ligature de celles-ci grâce au mécanisme de Jonction d’Extrémités Non Homologues (JENH). Au contraire, les CDB à une seule extrémité, faute d’une autre extrémité pour être réparées par JENH, doivent recourir au mécanisme plus complexe de la Recombinaison Homologue (RH). La RH reconstitue l’information génétique altérée en utilisant la copie de la région cassée produite lors de la duplication de l’ADN. En limitant la toxicité des CDB, ces deux voies de réparation conditionnent donc l’efficacité des thérapies anticancéreuses. En présence de CBD, elles sont potentiellement en compétition et nécessitent d’être coordonnées.
La façon dont la réparation d’une CDB s’oriente vers l’une ou l’autre des voies possibles est l’objet de cette étude. Des travaux précèdent du CNRS avaient établi qu’une étape essentielle de la réparation des CDB à une extrémité par la RH est l’éviction de la protéine Ku qui initie la JENH. Dans cette nouvelle publication, les scientifiques montrent qu’ATM, la principale protéine kinase activée par les CDB, a un rôle essentiel pour orienter la réparation vers la RH en phosphorylant plusieurs substrats, dont le complexe nucléase CtIP-MRN et la protéine de JENH DNA-PKcs. Ces phosphorylations sont nécessaires pour permettre le détachement des protéines de JENH de l’extrémité des CDB, empêchant de facto ce mécanisme de réparation d’opérer. L’inhibition d’ATM bloque l’éviction de Ku et des protéines associées, et conduit à la ligature inappropriée par la JENH des extrémités de CDB distantes, produisant des aberrations chromosomiques et aboutissant ainsi à la mort cellulaire.
Plusieurs candidats médicaments ont été développés pour inhiber ATM. Ces travaux ouvrent la voie à l’utilisation de ces inhibiteurs pour augmenter l’efficacité des thérapies anticancéreuses basées sur la production de CDB à une extrémité.
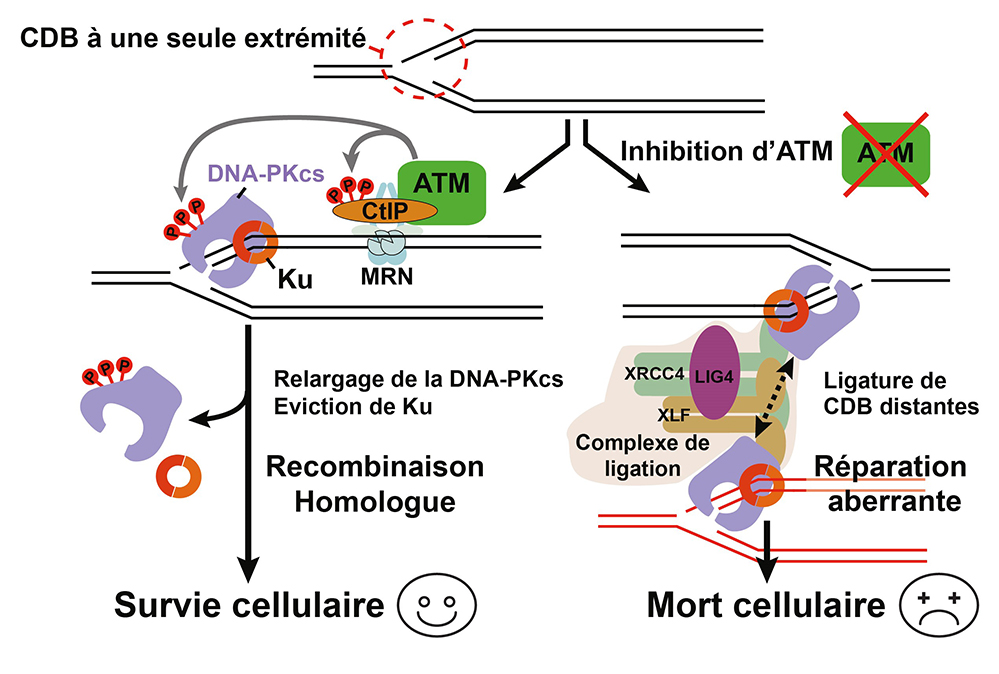
Figure: La réparation correcte des CDBs à une seule extrémité (panneau de gauche) nécessite la phosphorylation par la kinase ATM du complexe nucléase CtIP-MRN et de la protéine de JENH DNA-PKcs. Ces phosphorylations sont nécessaires à l’élimination des protéines de JENH des extrémités des CDBs. Lorsque ATM est inhibée (panneau de droite), les protéines de JENH s’accumulent de façon stable sur les CDBs et des produits de réparation toxiques sont générés conduisant à la mort cellulaire.
Pour en savoir plus:
ATM antagonizes NHEJ proteins assembly and DNA-ends synapsis at single-ended DNA double strand breaks.
Britton S, Chanut P, Delteil C, Barboule N, Frit P, Calsou P.
Nucleic Acids Res. 2020 Sep 5:gkaa723. doi: 10.1093/nar/gkaa723. Online ahead of print.
PMID: 32890395
Contact
Laboratoire
Institut de Pharmacologie et Biologie Structurale (IPBS) - (CNRS/Université de Toulouse)
route de Narbonne, 31077 Toulouse Cedex 4
